Category:Cluster analysis
Перейти к навигации
Перейти к поиску
разбиение на подсистемы | |||||
| Медиафайл | |||||
| Подкласс от | |||||
|---|---|---|---|---|---|
| Является частью | |||||
| Тематически относится к | |||||
| Используется как/для/в |
| ||||
| |||||
Подкатегории
В этой категории отображается 5 подкатегорий из имеющихся 5.
Страницы в категории «Cluster analysis»
Эта категория содержит единственную страницу.
Файлы в категории «Cluster analysis»
Показаны 189 файлов из 189, находящихся в данной категории.
-
10 תמונה.jpg 565 × 327; 44 Кб
-
4 תמונה.jpg 112 × 99; 3 Кб
-
-
-
-
-
-
-
-
-
-
-
-
-
-
-
-
-
-
-
-
-
-
-
-
-
Calcium-imaging-of-sleep–wake-related-neuronal-activity-in-the-dorsal-pons-ncomms10763-s2.ogv 38 с, 514 × 294; 4,04 Мб
-
Calcium-imaging-of-sleep–wake-related-neuronal-activity-in-the-dorsal-pons-ncomms10763-s3.ogv 28 с, 514 × 294; 1,33 Мб
-
-
Cluster-1.gif 601 × 402; 2 Кб
-
Cluster-1.svg 601 × 402; 2 Кб
-
Cluster-2.png 601 × 402; 1 Кб
-
Cluster-2.svg 601 × 402; 2 Кб
-
ClusterAnalysis Mouse de.svg 1355 × 547; 305 Кб
-
ClusterAnalysis Mouse.svg 1355 × 547; 308 Кб
-
Clustering nutrients01.png 666 × 667; 21 Кб
-
Clustering nutrients02.png 671 × 672; 25 Кб
-
Clusters.PNG 266 × 260; 15 Кб
-
Clusters.svg 250 × 251; 9 Кб
-
Clustersgeometricos.jpg 637 × 333; 13 Кб
-
Clustezinho.jpg 576 × 371; 18 Кб
-
-
-
Complete linkage Dendrogram 5S data.svg 1061 × 531; 18 Кб
-
-
-
DataClustering ElbowCriterion.JPG 355 × 266; 12 Кб
-
DBSCAN-density-data.svg 320 × 322; 77 Кб
-
DBSCAN-Gaussian-data.svg 434 × 467; 407 Кб
-
DBSCAN-Illustration.svg 165 × 119; 13 Кб
-
Decision stream.gif 1750 × 1742; 116 Кб
-
-
-
-
Different types of biclusters.jpg 1152 × 576; 33 Кб
-
Dynamic-Conformational-Changes-in-MUNC18-Prevent-Syntaxin-Binding-pcbi.1001097.s005.ogv 0,0 с, 1152 × 784; 20,28 Мб
-
Elbow in Inertia on uniform data.png 882 × 468; 23 Кб
-
Electroencephalographic-Brain-Dynamics-Following-Manually-Responded-Visual-Targets-pbio.0020176.v001.ogv 7,3 с, 640 × 480; 1001 Кб
-
EM Clustering of Old Faithful data.gif 360 × 309; 113 Кб
-
Em old faithful.gif 360 × 360; 272 Кб
-
EM-density-data.svg 434 × 467; 322 Кб
-
EM-Gaussian-data.svg 434 × 467; 413 Кб
-
Evolution-of-Collective-Behaviors-for-a-Real-Swarm-of-Aquatic-Surface-Robots-pone.0151834.s002.ogv 45 с, 1920 × 1080; 9,2 Мб
-
-
-
-
Example 1 KHOPCA.png 719 × 724; 69 Кб
-
Family-based-clusters-of-cognitive-test-performance-in-familial-schizophrenia-1471-244X-4-20-S5.ogv 0,8 с, 656 × 704; 1,49 Мб
-
-
GaussienChevauche1.gif 960 × 560; 8 Кб
-
GaussienChevauche2.gif 960 × 560; 11 Кб
-
Gene-expression-profiles-in-skeletal-muscle-after-gene-electrotransfer-1471-2199-8-56-S10.ogv 35 с, 320 × 240; 6,28 Мб
-
Gene-expression-profiles-in-skeletal-muscle-after-gene-electrotransfer-1471-2199-8-56-S11.ogv 21 с, 320 × 240; 2,95 Мб
-
Gene-expression-profiles-in-skeletal-muscle-after-gene-electrotransfer-1471-2199-8-56-S12.ogv 35 с, 320 × 240; 5,21 Мб
-
Gene-expression-profiles-in-skeletal-muscle-after-gene-electrotransfer-1471-2199-8-56-S13.ogv 15 с, 320 × 240; 2,54 Мб
-
Gene-expression-profiles-in-skeletal-muscle-after-gene-electrotransfer-1471-2199-8-56-S14.ogv 35 с, 320 × 240; 5,22 Мб
-
Gene-expression-profiles-in-skeletal-muscle-after-gene-electrotransfer-1471-2199-8-56-S15.ogv 8,9 с, 320 × 240; 1,53 Мб
-
Gene-expression-profiles-in-skeletal-muscle-after-gene-electrotransfer-1471-2199-8-56-S16.ogv 35 с, 320 × 240; 5,35 Мб
-
Gene-expression-profiles-in-skeletal-muscle-after-gene-electrotransfer-1471-2199-8-56-S17.ogv 12 с, 320 × 240; 2,1 Мб
-
Gene-expression-profiles-in-skeletal-muscle-after-gene-electrotransfer-1471-2199-8-56-S18.ogv 35 с, 320 × 240; 5,41 Мб
-
Gene-expression-profiles-in-skeletal-muscle-after-gene-electrotransfer-1471-2199-8-56-S19.ogv 11 с, 320 × 240; 2,14 Мб
-
Gene-expression-profiles-in-skeletal-muscle-after-gene-electrotransfer-1471-2199-8-56-S4.ogv 35 с, 320 × 240; 6,35 Мб
-
Gene-expression-profiles-in-skeletal-muscle-after-gene-electrotransfer-1471-2199-8-56-S5.ogv 15 с, 320 × 240; 2,32 Мб
-
Gene-expression-profiles-in-skeletal-muscle-after-gene-electrotransfer-1471-2199-8-56-S6.ogv 35 с, 320 × 240; 6,26 Мб
-
Gene-expression-profiles-in-skeletal-muscle-after-gene-electrotransfer-1471-2199-8-56-S7.ogv 18 с, 320 × 240; 2,77 Мб
-
Gene-expression-profiles-in-skeletal-muscle-after-gene-electrotransfer-1471-2199-8-56-S8.ogv 35 с, 320 × 240; 6,22 Мб
-
Gene-expression-profiles-in-skeletal-muscle-after-gene-electrotransfer-1471-2199-8-56-S9.ogv 19 с, 320 × 240; 2,84 Мб
-
-
-
GLPK solution of a clustering problem.svg 1200 × 1200; 108 Кб
-
-
-
Hierarchical1.jpg 410 × 209; 18 Кб
-
IdentifiabilityZones.pdf 1500 × 1500; 231 Кб
-
-
-
-
Iris silhouette.svg 630 × 630; 325 Кб
-
K-means centre force.gif 360 × 430; 12 Кб
-
K-means convergence.gif 637 × 619; 499 Кб
-
K-means steg 1.svg 512 × 534; 6 Кб
-
K-means steg 2.svg 512 × 534; 7 Кб
-
K-means steg 3.svg 512 × 534; 13 Кб
-
K-means steg 4.svg 512 × 535; 8 Кб
-
K-means.png 9350 × 3567; 1,37 Мб
-
K-Medoids Clustering.gif 756 × 756; 154 Кб
-
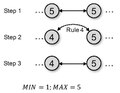
KHOPCA rule 4.pdf 493 × 383; 28 Кб
-
-
-
-
-
-
-
-
-
Live-imaging-and-analysis-of-postnatal-mouse-retinal-development-1471-213X-13-24-S7.ogv 16 с, 1008 × 326; 2,19 Мб
-
LOF-idea.svg 124 × 130; 8 Кб
-
-
Maturation-of-Induced-Pluripotent-Stem-Cell-Derived-Hepatocytes-by-3D-Culture-pone.0086372.s018.ogv 9,1 с, 480 × 480; 998 Кб
-
Maturation-of-Induced-Pluripotent-Stem-Cell-Derived-Hepatocytes-by-3D-Culture-pone.0086372.s019.ogv 4,8 с, 512 × 512; 557 Кб
-
Maturation-of-Induced-Pluripotent-Stem-Cell-Derived-Hepatocytes-by-3D-Culture-pone.0086372.s020.ogv 4,8 с, 1024 × 1024; 741 Кб
-
Maturation-of-Induced-Pluripotent-Stem-Cell-Derived-Hepatocytes-by-3D-Culture-pone.0086372.s021.ogv 4,8 с, 1024 × 1024; 583 Кб
-
Microgravity-simulation-by-diamagnetic-levitation-effects-of-a-strong-gradient-magnetic-field-on-1471-2164-13-52-S2.ogv 10 м 0 с, 640 × 480; 81,26 Мб
-
Minimum spannig tree.jpg 575 × 369; 18 Кб
-
-
Nearest-neighbor chain algorithm animated.gif 300 × 311; 449 Кб
-
Nonbayesian-categorical-mixture.svg 178 × 156; 16 Кб
-
Nonbayesian-gaussian-mixture.svg 186 × 154; 20 Кб
-
Occupied Grids P = 0.24.png 394 × 366; 12 Кб
-
Occupied Grids P = 0.64.png 404 × 378; 14 Кб
-
OPTICS-Gaussian-data.svg 434 × 467; 569 Кб
-
OPTICS.png 350 × 341; 31 Кб
-
OPTICS.svg 712 × 487; 643 Кб
-
Otimalidadedoalgoritmo.jpeg 700 × 400; 23 Кб
-
PACexplained.png 720 × 540; 70 Кб
-
Plasticity-of-Blood--and-Lymphatic-Endothelial-Cells-and-Marker-Identification-pone.0074293.s002.ogv 23 с, 1280 × 720; 2,88 Мб
-
Primsdem.jpg 700 × 400; 7 Кб
-
Principal tree for Iris data set.png 1240 × 720; 36 Кб
-
-
RDQGif.gif 461 × 560; 6 Кб
-
Reachability-distance.svg 124 × 130; 6 Кб
-
School cluster.png 4096 × 4096; 5,79 Мб
-
-
-
-
-
Simple linkage-5S.svg 776 × 584; 2 Кб
-
Single linkage.png 899 × 537; 17 Кб
-
Singlelink.jpg 437 × 172; 9 Кб
-
Singlelinkage.jpg 190 × 163; 3 Кб
-
SLINK-density-data.svg 434 × 467; 445 Кб
-
SLINK-Gaussian-data.svg 434 × 467; 572 Кб
-
Spatial genetic structure of walnuts population.png 2242 × 1055; 822 Кб
-
-
Specclus irisknn1.svg 900 × 900; 4,81 Мб
-
Spectral clustering vs k means.png 4000 × 1947; 77 Кб
-
Spectral clusterization example.png 605 × 509; 39 Кб
-
Stereo-Vision-Tracking-of-Multiple-Objects-in-Complex-Indoor-Environments-sensors-10-08865-s001.ogv 2,9 с, 320 × 480; 541 Кб
-
SubspaceClustering.png 300 × 293; 27 Кб
-
Super-resolution-mapping-of-glutamate-receptors-in-C.-elegans-by-confocal-correlated-PALM-srep13532-s1.ogv 2,5 с, 2156 × 1320; 2,87 Мб
-
-
Swedish defense Twitter mentionsgraph cluster.png 1754 × 1239; 1,19 Мб
-
Swiss cmeans.svg 630 × 630; 109 Кб
-
-
-
The-ligand-binding-mechanism-to-purine-nucleoside-phosphorylase-elucidated-via-molecular-dynamics-ncomms7155-s2.ogv 1 м 9 с, 480 × 270; 21,12 Мб
-
The-ligand-binding-mechanism-to-purine-nucleoside-phosphorylase-elucidated-via-molecular-dynamics-ncomms7155-s3.ogv 2 м 25 с, 480 × 270; 62,62 Мб
-
The-ligand-binding-mechanism-to-purine-nucleoside-phosphorylase-elucidated-via-molecular-dynamics-ncomms7155-s4.ogv 1 м 3 с, 480 × 270; 20,26 Мб
-
The-ligand-binding-mechanism-to-purine-nucleoside-phosphorylase-elucidated-via-molecular-dynamics-ncomms7155-s5.ogv 4 м 5 с, 480 × 270; 99,36 Мб
-
The-Neuromagnetic-Dynamics-of-Time-Perception-pone.0042618.s001.ogv 4,8 с, 288 × 288; 35 Кб
-
The-Neuromagnetic-Dynamics-of-Time-Perception-pone.0042618.s002.ogv 4,8 с, 288 × 288; 73 Кб
-
Truth table IV.PNG 958 × 638; 153 Кб
-
Tumor-Invasion-Optimization-by-Mesenchymal-Amoeboid-Heterogeneity-srep10622-s2.ogv 17 с, 640 × 480; 1,56 Мб
-
Tumor-Invasion-Optimization-by-Mesenchymal-Amoeboid-Heterogeneity-srep10622-s3.ogv 17 с, 640 × 480; 1,36 Мб
-
Tumor-Invasion-Optimization-by-Mesenchymal-Amoeboid-Heterogeneity-srep10622-s4.ogv 17 с, 640 × 480; 1,32 Мб
-
Tumor-Invasion-Optimization-by-Mesenchymal-Amoeboid-Heterogeneity-srep10622-s5.ogv 17 с, 640 × 480; 1,19 Мб
-
Unfolding-Simulations-Reveal-the-Mechanism-of-Extreme-Unfolding-Cooperativity-in-the-Kinetically-pcbi.1000689.s007.ogv 2 м 49 с, 280 × 240; 30,84 Мб
-
UPGMA Dendrogram 5S data.svg 900 × 675; 25 Кб
-
UPGMA Dendrogram Hierarchical.svg 937 × 597; 25 Кб
-
Visualizing-and-clustering-high-throughput-sub-cellular-localization-imaging-1471-2105-9-81-S1.ogv 48 с, 534 × 400; 3,55 Мб
-
Visualizing-and-clustering-high-throughput-sub-cellular-localization-imaging-1471-2105-9-81-S2.ogv 48 с, 534 × 400; 3,55 Мб
-
Visualizing-and-clustering-high-throughput-sub-cellular-localization-imaging-1471-2105-9-81-S3.ogv 41 с, 534 × 400; 3,66 Мб
-
WPGMA Dendrogram 5S data.svg 900 × 675; 24 Кб
-
Wykres 1.1.jpg 1361 × 704; 30 Кб
-
תמונה 14.jpg 566 × 318; 81 Кб
-
תמונה 5.jpg 99 × 92; 4 Кб
-
תמונה 6.jpg 104 × 97; 4 Кб
-
תמונה 7.jpg 82 × 79; 3 Кб
-
תמונה 9.jpg 552 × 314; 52 Кб