Category:X-ray diffraction
ナビゲーションに移動
検索に移動
English: X-ray scattering techniques are a family of non-destructive analytical techniques which reveal information about the crystallographic structure, chemical composition, and physical properties of materials and thin films. This category groups media relating to X-ray diffraction and crystallography.
日本語: X線回折
中文:X光衍射
Nederlands: Röntgendiffractie
family of non-destructive analytical techniques | |||||
| メディアをアップロード | |||||
| 上位クラス | |||||
|---|---|---|---|---|---|
| |||||
下位カテゴリ
このカテゴリに属する 22 個のサブカテゴリのうち、 22 個を表示しています。
- Energy-dispersive X-ray diffraction (1ファイル)
A
- Area detector diffractometer (11ファイル)
B
- Buerger precession camera (2ファイル)
D
- De Jong-Bouman retigraph camera (1ファイル)
E
F
- Friedel's law (3ファイル)
I
K
L
M
P
S
- Single-crystal x-ray diffraction (3ファイル)
- Small-angle X-ray scattering (SAXS) (5ファイル)
V
- Videos of x-ray diffraction (1ファイル)
W
- Weissenberg camera (1ファイル)
X
- X-ray diffraction in biology (4ファイル)
- X-ray diffraction pattern (3ファイル)
- X-ray diffraction spectrum (4ファイル)
カテゴリ「X-ray diffraction」にあるメディア
このカテゴリに属する 277 個のファイルのうち、 200 個を表示しています。
(前のページ) (次のページ)-
A B DNA XR ar.jpg 708 × 897;250キロバイト
-
-
A-pain-inducing-centipede-toxin-targets-the-heat-activation-machinery-of-nociceptor-TRPV1-ncomms9297-s2.ogv 31秒、 1,109 × 924;31.91メガバイト
-
-
-
ABDNAxrgpj.jpg 720 × 960;63キロバイト
-
An-electrostatic-mechanism-for-Ca2+-mediated-regulation-of-gap-junction-channels-ncomms9770-s2.ogv 2.8秒、 640 × 480;111キロバイト
-
An-electrostatic-mechanism-for-Ca2+-mediated-regulation-of-gap-junction-channels-ncomms9770-s3.ogv 2.8秒、 680 × 480;149キロバイト
-
An-electrostatic-mechanism-for-Ca2+-mediated-regulation-of-gap-junction-channels-ncomms9770-s4.ogv 39秒、 752 × 1,056;58.48メガバイト
-
An-electrostatic-mechanism-for-Ca2+-mediated-regulation-of-gap-junction-channels-ncomms9770-s5.ogv 42秒、 752 × 640;19.16メガバイト
-
An-electrostatic-mechanism-for-Ca2+-mediated-regulation-of-gap-junction-channels-ncomms9770-s6.ogv 42秒、 752 × 640;19.83メガバイト
-
An-electrostatic-mechanism-for-Ca2+-mediated-regulation-of-gap-junction-channels-ncomms9770-s7.ogv 40秒、 752 × 1,056;63.66メガバイト
-
An-extended-U2AF65–RNA-binding-domain-recognizes-the-3′-splice-site-signal-ncomms10950-s2.ogv 21秒、 740 × 487;14.09メガバイト
-
An-in-cellulo-derived-structure-of-PAK4-in-complex-with-its-inhibitor-Inka1-ncomms9681-s2.ogv 31秒、 746 × 420;9.55メガバイト
-
An-in-cellulo-derived-structure-of-PAK4-in-complex-with-its-inhibitor-Inka1-ncomms9681-s3.ogv 17秒、 400 × 226;319キロバイト
-
An-in-cellulo-derived-structure-of-PAK4-in-complex-with-its-inhibitor-Inka1-ncomms9681-s4.ogv 8.6秒、 320 × 180;86キロバイト
-
An-in-cellulo-derived-structure-of-PAK4-in-complex-with-its-inhibitor-Inka1-ncomms9681-s5.ogv 21秒、 640 × 360;1.11メガバイト
-
An-in-cellulo-derived-structure-of-PAK4-in-complex-with-its-inhibitor-Inka1-ncomms9681-s6.ogv 11秒、 1,296 × 730;3.73メガバイト
-
An-in-cellulo-derived-structure-of-PAK4-in-complex-with-its-inhibitor-Inka1-ncomms9681-s7.ogv 8.2秒、 1,280 × 720;6.55メガバイト
-
Anomalous Friedel pairs.svg 693 × 693;8キロバイト
-
Anomalous structure factor.svg 990 × 765;13キロバイト
-
AryloA2.png 885 × 590;339キロバイト
-
-
BeheneatodePlata-DifraccionXBajoAngulo.png 495 × 496;150キロバイト
-
Beugungsbild eines Kristalls.png 500 × 500;72キロバイト
-
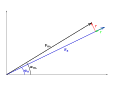
Bragg's law.svg 1,100 × 500;7キロバイト
-
BraggDiffraction2.svg 211 × 202;4キロバイト
-
-
-
-
Cambios en los mapas de densidad.jpg 385 × 155;32キロバイト
-
-
Caulobacter crescentus CcrM.png 1,452 × 1,536;756キロバイト
-
-
-
Crambin P41 hi-res map 3nir.tiff 1,024 × 768;695キロバイト
-
Cromer-Mann structure factors.svg 1,000 × 1,000;20キロバイト
-
-
CSIRO ScienceImage 2386 XRay Crystallography.jpg 473 × 638;208キロバイト
-
CSIRO ScienceImage 426 XRay Crystallography Equipment.jpg 2,571 × 1,715;3.93メガバイト
-
Cu-fp-fpp.png 640 × 480;4キロバイト
-
CuZn SOD precession photo C2.jpg 550 × 550;215キロバイト
-
Daños.jpg 567 × 145;35キロバイト
-
DBP 1979 1021 Max von Laue Röntgenstrahl-Beugung am Kristallgitter.jpg 1,070 × 670;458キロバイト
-
Dials17 indexing ambiguity clustering.gif 800 × 600;85キロバイト
-
Dials17 myo indexing ambiguity.png 497 × 937;78キロバイト
-
Difference Fourier map (heavy atom method).png 856 × 677;234キロバイト
-
Diffraction facteur forme.png 519 × 365;12キロバイト
-
Diffraction facteur struct.png 327 × 189;4キロバイト
-
Diffusion rayleigh et diffraction.png 786 × 234;11キロバイト
-
Diffusion rayleigh et diffraction.svg 811 × 265;173キロバイト
-
Difracção de Raios-X a partir de planos atómicos..png 501 × 246;7キロバイト
-
Difração de raios x.png 1,381 × 658;1.7メガバイト
-
-
-
-
-
-
-
-
Dispersion1.jpg 227 × 316;10キロバイト
-
DOSBIW.png 1,200 × 1,199;146キロバイト
-
DOSBIWoneRotamer.png 1,200 × 1,199;104キロバイト
-
Double slit x-ray simulation 0000mm log-grayscale.jpg 500 × 500;4キロバイト
-
Double slit x-ray simulation 0020mm log-grayscale.jpg 500 × 500;7キロバイト
-
Double slit x-ray simulation 0050mm log-grayscale.jpg 500 × 500;9キロバイト
-
Double slit x-ray simulation 0100mm log-grayscale.jpg 500 × 500;9キロバイト
-
Double slit x-ray simulation 0200mm log-grayscale.jpg 500 × 500;10キロバイト
-
Double slit x-ray simulation 0400mm log-grayscale.jpg 500 × 500;12キロバイト
-
Double slit x-ray simulation 0600mm log-grayscale.jpg 500 × 500;23キロバイト
-
Double slit x-ray simulation monochromatic blue-white.png 2,000 × 1,500;329キロバイト
-
Double slit x-ray simulation monochromatic grayscale.jpg 2,000 × 1,500;103キロバイト
-
Double slit x-ray simulation polychromatic false-color.jpg 2,000 × 1,500;129キロバイト
-
Double slit x-ray simulation trans-long 05000 eV.jpg 1,000 × 1,000;44キロバイト
-
Double slit x-ray simulation trans-long 07500 eV.jpg 1,000 × 1,000;42キロバイト
-
Double slit x-ray simulation trans-long 10000 eV.jpg 1,000 × 1,000;41キロバイト
-
Double slit x-ray simulation trans-long 12500 eV.jpg 1,000 × 1,000;41キロバイト
-
Double slit x-ray simulation trans-long 15000 eV.jpg 1,000 × 1,000;40キロバイト
-
DoxyIAM.png 1,246 × 966;4.6メガバイト
-
DoxyMM.png 1,246 × 966;4.6メガバイト
-
Drehkristall.png 734 × 602;11キロバイト
-
Drug-Export-Pathway-of-Multidrug-Exporter-AcrB-Revealed-by-DARPin-Inhibitors-pbio.0050007.sv001.ogv 12秒、 768 × 576;9.82メガバイト
-
DRX amorphe.png 619 × 339;18キロバイト
-
DRX mésophases.JPG 315 × 214;8キロバイト
-
-
Dyfraktometr rentgenowski (XRD).JPG 2,000 × 3,008;2.24メガバイト
-
Ecuacion1.jpg 567 × 266;28キロバイト
-
Ed maleinanhydrid.png 759 × 558;28キロバイト
-
-
-
-
-
-
-
-
-
-
Equipo de difracción de rayos X 01.jpg 7,500 × 5,062;10.94メガバイト
-
Equipo de difracción de rayos X 02.jpg 5,166 × 7,500;11.14メガバイト
-
Equipo de difracción de rayos X 03.jpg 4,203 × 7,500;10.15メガバイト
-
Esquema DRX.jpg 802 × 406;145キロバイト
-
Etude des cristaux par diffraction des rayonnements-Musée de minéralogie de Strasbourg (1).JPG 3,240 × 4,320;4.64メガバイト
-
Etude des cristaux par diffraction des rayonnements-Musée de minéralogie de Strasbourg (2).jpg 2,352 × 2,740;1.29メガバイト
-
Ewald Sphere Example.png 1,396 × 1,110;148キロバイト
-
Ewald.gif 628 × 658;16キロバイト
-
FibDiffTiltDemo.gif 320 × 240;1.41メガバイト
-
-
-
-
Fitting a model into electron density.gif 200 × 141;648キロバイト
-
-
Fouriertransformation2-og.jpg 945 × 695;173キロバイト
-
Freezed XRD.jpg 3,397 × 2,290;2.91メガバイト
-
GC-MS in foreground and an X-Ray diffractometer in background.jpg 3,264 × 2,448;1.93メガバイト
-
GFPs-Mechanical-Intermediate-States-pone.0046962.s003.ogv 1分 9秒、 852 × 480;23.95メガバイト
-
GonioX.jpg 640 × 480;85キロバイト
-
GroEL resolution series.png 2,668 × 742;1.98メガバイト
-
Hand-made XRD-structure.jpg 1,280 × 960;294キロバイト
-
Heavy atom.png 404 × 310;13キロバイト
-
Hemisphere of Diffraction.png 524 × 395;31キロバイト
-
Hemoglobin E (Glu26Lys) 1yvt.png 640 × 480;298キロバイト
-
High School Student Conducting a X-Ray Diffraction Test.jpg 1,069 × 1,061;179キロバイト
-
-
Hot-Melt-Extruded-Amorphous-Solid-Dispersion-of-Posaconazole-with-Improved-Bioavailability-146781.f1.ogv 1分 55秒、 640 × 480;36.24メガバイト
-
Human intelectin-1 ligand binding site.jpg 4,375 × 3,125;1.52メガバイト
-
Identification-of-pyrazolopyridazinones-as-PDEδ-inhibitors-ncomms11360-s1.ogv 9.0秒、 671 × 512;2.61メガバイト
-
Identification-of-pyrazolopyridazinones-as-PDEδ-inhibitors-ncomms11360-s2.ogv 9.0秒、 671 × 512;2.91メガバイト
-
Identification-of-pyrazolopyridazinones-as-PDEδ-inhibitors-ncomms11360-s3.ogv 9.0秒、 671 × 512;3.52メガバイト
-
Identification-of-pyrazolopyridazinones-as-PDEδ-inhibitors-ncomms11360-s4.ogv 9.0秒、 671 × 512;3.27メガバイト
-
Identification-of-pyrazolopyridazinones-as-PDEδ-inhibitors-ncomms11360-s5.ogv 9.0秒、 671 × 512;4.61メガバイト
-
Identification-of-pyrazolopyridazinones-as-PDEδ-inhibitors-ncomms11360-s6.ogv 9.0秒、 671 × 512;2.34メガバイト
-
Identification-of-the-Allosteric-Regulatory-Site-of-Insulysin-pone.0020864.s012.ogv 4.0秒、 1,280 × 720;669キロバイト
-
Identification-of-the-Allosteric-Regulatory-Site-of-Insulysin-pone.0020864.s013.ogv 4.0秒、 1,280 × 720;405キロバイト
-
-
-
-
-
-
Interferentiepatroon door C.H.Wind.jpg 496 × 924;136キロバイト
-
-
-
-
Isomorphous replacement.png 404 × 310;13キロバイト
-
Ketosteroid Isomerase Image 1.jpg 808 × 516;69キロバイト
-
Ketosteroid Isomerase Image 2.jpg 808 × 516;69キロバイト
-
-
LATTICE PLANES.PNG 874 × 350;26キロバイト
-
LOV2 domain of phototropin-2 protein from Arabidopsis thaliana.png 970 × 819;373キロバイト
-
Lysozym diffraction.png 549 × 549;240キロバイト
-
Macromolecular-Crystallography-beamline.png 1,712 × 1,368;3.21メガバイト
-
Mapa de densidad1.jpg 482 × 360;72キロバイト
-
-
-
MiTeGen Crystal Mounts.jpg 6,000 × 4,000;7.34メガバイト
-
Modeling-a-New-Water-Channel-That-Allows-SET9-to-Dimethylate-p53-pone.0019856.s005.ogv 10秒、 656 × 624;1.87メガバイト
-
-
-
-
Monomeric human intelectin-1.png 500 × 700;181キロバイト
-
Monomeric XEEL.png 500 × 700;190キロバイト
-
Motion-and-Flexibility-in-Human-Cytochrome-P450-Aromatase-pone.0032565.s011.ogv 56秒、 480 × 360;3.85メガバイト
-
Motion-and-Flexibility-in-Human-Cytochrome-P450-Aromatase-pone.0032565.s012.ogv 1分 5秒、 480 × 360;4.04メガバイト
-
Motion-and-Flexibility-in-Human-Cytochrome-P450-Aromatase-pone.0032565.s013.ogv 52秒、 480 × 360;6.07メガバイト
-
Motion-and-Flexibility-in-Human-Cytochrome-P450-Aromatase-pone.0032565.s014.ogv 1分 5秒、 640 × 360;15.66メガバイト
-
Motion-and-Flexibility-in-Human-Cytochrome-P450-Aromatase-pone.0032565.s015.ogv 1分 36秒、 480 × 360;8.03メガバイト
-
Motion-and-Flexibility-in-Human-Cytochrome-P450-Aromatase-pone.0032565.s016.ogv 1分 38秒、 480 × 360;6.03メガバイト
-
Motion-and-Flexibility-in-Human-Cytochrome-P450-Aromatase-pone.0032565.s017.ogv 2分 51秒、 480 × 360;14.38メガバイト
-
-
Observing-the-overall-rocking-motion-of-a-protein-in-a-crystal-ncomms9361-s2.ogv 20秒、 336 × 336;8.56メガバイト
-
Observing-the-overall-rocking-motion-of-a-protein-in-a-crystal-ncomms9361-s3.ogv 20秒、 336 × 336;8.32メガバイト
-
Observing-the-overall-rocking-motion-of-a-protein-in-a-crystal-ncomms9361-s4.ogv 20秒、 336 × 336;8.52メガバイト
-
OH bond charge density resulting from IAM.png 1,680 × 1,680;8.09メガバイト
-
OH bond charge density resulting from MM.png 1,680 × 1,680;8.09メガバイト
-
Original Richards box photo.jpg 400 × 568;109キロバイト
-
Oxygen form factor - e & X.png 1,468 × 1,099;22キロバイト
-
P450arom.png 1,700 × 999;451キロバイト
-
Patterson map.svg 882 × 234;5キロバイト
-
Penicillin.png 1,460 × 928;277キロバイト
-
Phosphoinositide-mediated-oligomerization-of-a-defensin-induces-cell-lysis-elife01808v001.ogv 20秒、 512 × 512;3.2メガバイト
-
Phosphoinositide-mediated-oligomerization-of-a-defensin-induces-cell-lysis-elife01808v002.ogv 12秒、 330 × 330;147キロバイト
-
Phosphoinositide-mediated-oligomerization-of-a-defensin-induces-cell-lysis-elife01808v003.ogv 20秒、 194 × 194;1.29メガバイト
-
Phosphoinositide-mediated-oligomerization-of-a-defensin-induces-cell-lysis-elife01808v004.ogv 12秒、 530 × 512;571キロバイト
-
Phosphoinositide-mediated-oligomerization-of-a-defensin-induces-cell-lysis-elife01808v005.ogv 21秒、 1,387 × 1,109;5.03メガバイト
-
Phosphoinositide-mediated-oligomerization-of-a-defensin-induces-cell-lysis-elife01808v006.ogv 30秒、 295 × 295;412キロバイト
-
Phosphoinositide-mediated-oligomerization-of-a-defensin-induces-cell-lysis-elife01808v007.ogv 40秒、 267 × 267;880キロバイト
-
PIXRD 001.PNG 493 × 397;22キロバイト
-
Platform for protein crystallography and X-ray scattering.jpg 3,000 × 2,000;1.26メガバイト
-
PRIME advanced options.png 974 × 889;57キロバイト
-
PRIME main.png 1,596 × 958;94キロバイト
-
Protein crystal.jpg 198 × 152;46キロバイト
-
Raios X reflexão e deflexão.png 504 × 203;5キロバイト
-
Rate of Protein Structure Determination-2014.png 3,500 × 2,500;228キロバイト
-
Rate of Protein Structure Determination-2019a.png 2,283 × 1,141;342キロバイト
-
Rate of Protein Structure Determination-2019b.png 2,283 × 1,088;918キロバイト
-
Rayons X Philips-Musée de minéralogie de Strasbourg (2).jpg 3,201 × 3,074;2.03メガバイト
-
-
-
-
Reciprocal monoclinic lattice.png 516 × 318;126キロバイト