File:Tiger phylogenetic relationships.png
De Wikimedia Commons, el repositorio multimedia libre
Ir a la navegación
Ir a la búsqueda
Tamaño de esta previsualización: 574 × 600 píxeles. Otras resoluciones: 230 × 240 píxeles | 460 × 480 píxeles | 735 × 768 píxeles | 980 × 1024 píxeles | 2001 × 2090 píxeles.
Archivo original (2001 × 2090 píxeles; tamaño de archivo: 684 kB; tipo MIME: image/png)
Información del archivo
Datos estructurados
Leyendas
Leyendas
Añade una explicación corta acerca de lo que representa este archivo
Resumen[editar]
| DescripciónTiger phylogenetic relationships.png |
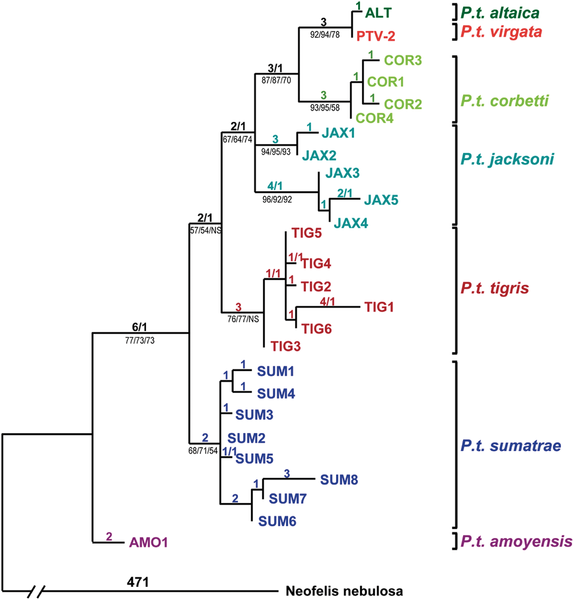
English: Haplotype designations are color coded by subspecies of the tigers that carried them. PTV-2 is a Caspian tiger (Panthera tigris virgata) specimen for which all gene segments attempted (1257 bp) in Caspian tigers were successfully sequenced. Other Caspian tigers produced partial sequences identical to PTV-2. The only exceptions were three individuals, each displaying a single derived nucleotide difference when compared to PTV-2 (found only in that individual and in no other tigers of any subspecies). Likewise, the only mtDNA haplotype carried by Amur or “Siberian” tigers (P. t. altaica) proved to be a single derived step away from the haplotype of PTV-2, suggesting a close relationship between the Amur and Caspian tiger subspecies. Tiger haplotypes carried by all but the Caspian subspecies are from a previously published dataset, while a clouded leopard (Neofelis nebulosa) sequence (GenBank DQ257669) was used to root the tree. The tree depicted was inferred using maximum parsimony, with the number of steps/homoplasies listed above the branches, while (for major clades) bootstrap percentages are listed below branches for maximum parsimony, maximum likelihood and Neighbour Joining methods. We used full length mtDNA sequences of clouded leopard, leopard and snow leopard to root the tree; all combinations of 1, 2 or 3 outgroups yielded trees with similar topology to the one depicted, with the same basal position for the P. t. amoyensis AMO1 haplotype, and a close relationship between P.t. virgata and P. t. altaica haplotypes. doi:info:doi/10.1371/journal.pone.0004125.g002 |
||
| Fecha | |||
| Fuente | Driscoll CA, Yamaguchi N, Bar-Gal GK, Roca AL, Luo S, et al. (2009) Mitochondrial Phylogeography Illuminates the Origin of the Extinct Caspian Tiger and Its Relationship to the Amur Tiger. PLoS ONE 4(1): e4125. doi:10.1371/journal.pone.0004125 | ||
| Autor | Driscoll CA, Yamaguchi N, Bar-Gal GK, Roca AL, Luo S, et al. | ||
| Permiso (Reutilización de este archivo) |
|
Historial del archivo
Haz clic sobre una fecha y hora para ver el archivo tal como apareció en ese momento.
| Fecha y hora | Miniatura | Dimensiones | Usuario | Comentario | |
|---|---|---|---|---|---|
| actual | 10:41 26 feb 2012 |  | 2001 × 2090 (684 kB) | Pmaas (discusión | contribs.) |
No puedes sobrescribir este archivo.
Usos del archivo
La siguiente página usa este archivo:
Uso global del archivo
Las wikis siguientes utilizan este archivo:
- Uso en ar.wikipedia.org
- Uso en en.wikipedia.org
- Uso en es.wikipedia.org
- Uso en eu.wikipedia.org
- Uso en fa.wikipedia.org
- Uso en fr.wikipedia.org
- Uso en he.wikipedia.org
- Uso en hu.wikipedia.org
- Uso en ms.wikipedia.org
- Uso en no.wikipedia.org
- Uso en or.wikipedia.org
- Uso en outreach.wikimedia.org
- Uso en sq.wikipedia.org
- Uso en te.wikipedia.org
- Uso en tr.wikipedia.org
- Uso en vi.wikipedia.org
Metadatos
Este archivo contiene información adicional, probablemente añadida por la cámara digital o el escáner usado para crearlo o digitalizarlo.
Si el archivo ha sido modificado desde su estado original, pueden haberse perdido algunos detalles.
| Autor |
|
|---|---|
| Resolución horizontal | 118,11 dpc |
| Resolución vertical | 118,11 dpc |
| Software usado |
